细菌基因组 | rpoB的插入变异导致高度耐药性
链接:https://doi.org/10.1016/j.tube.2020.102015
前 言
在巴西南部的南里奥格兰德州研究发现,在耐多药结核分枝杆菌rpoB基因的435密码子处插入12个核苷酸 (nt),导致了4个氨基酸 (Q-N-N-P)重复,这种插入在世界上任何其他地区都没有报道。因此,为了加强巴西南部结核病控制管理,需要阐明12nt插入的分子和表型后果,以及对这种菌株传播到人群的理解。对于这一建议,基于WGS的研究方法筛选了南里奥格兰德州的耐RIF结核分枝杆菌菌株,以确定携带12nt插入的菌株。本文研究了这些菌株之间的系统进化 (Phylogenetic)关系,插入突变在抗性水平和生物学成本 (Biological cost)上的表型后果,以及对RIF结合效应的影响的计算机预测。
结 果
在南里奥格兰德州的174株耐RIF菌株中,有16株 (9.19%)在rpoB基因第435位密码子上进行了12nt插入,均为多重耐药株。根据药敏试验 (DST)结果,在这16株MDR菌株中,一株对乙胺丁醇 (EMB)额外耐药,另一株对链霉素 (STR)额外耐药。其中9人是囚犯,或在监狱里呆过一段时间,2人无家可归。这些囚犯来自4个不同的监狱机构。(文章结尾:12nt插入株有可能从监狱服刑人群传播到社区)
通过分析rpoB基因的核苷酸序列,发现12nt插入的发生情况略有不同。总体而言,12nt插入发生在对应于rpoB基因第435密码子的基因组位置761111。然而,在16株插入该基因的菌株中,有12株在761110位由腺嘌呤变为鸟嘌呤,导致第435位氨基酸发生替换 (GAC>GGC,Asp435Gly)。为了便于理解,将基因组位置761110处具有额外多态性的12个核苷酸插入命名为“rpoB INS1” (12/16),而将仅有12个nt插入命名为“rpoB INS2” (4/16)。此外,对两株同时携带rpoB INS1和rpoB INS2的菌株 (混合菌株)进行了Sanger测序,发现与基于NGS的测序没有差异。为了了解这种插入在全球其他菌株中可能发生的情况,基于在线工具TBDreaMDB、MUBII-TB-DB、ReSeqTB中的可用数据进行了审查,结果没有发现这种变异。
显示12个核苷酸插入的发生情况,INS1, INS2
根据SNP分型 (SNP-based typing),所有出现12nt插入的菌株均属于结核分枝杆菌第4亚型,4.3.3亚型,属于欧美系 (LAM RD115 sublineage)。同样,所有菌株都带有RD115缺失。在计算机分型 (In silico spoligotyping)中,有15株菌株具有相同的Spoligo型,属于Spoligo国际型 (SIT),以前被错误地鉴定为Mycobacterium pinnipedii。其余菌株在重复序列 (Direct repeat, DR)位点上缺失43个间隔 (Spacers),在SITVIT2数据库中被归类为ATYPIC (SIT 2669)。
此外,包括7个结核分枝杆菌谱系、4个亚系和其他4个不含12nt插入的SIT863菌株的基因组的系统进化推断表明,12nt插入的菌株与其他SIT863菌株 (下图浅绿色背景)的亲缘关系很近。基于WGS的系统进化分析揭示的另一个重要事实是,以5个SNPs为阈值,这16个菌株被聚为一个独特的基因组簇。
计算机预测药物结合效应
本研究模拟了INS1和INS2对RNAP结构的影响,以预测这些多态性对RIF和聚合酶之间相互作用的影响。首先先进行同源建模,随着同源模型的验证,使用对接程序 (Docking programs)来预测模型结构中的RIF相互作用。在表1中,可以观察到,与RNAP_INS1-RIF相互作用和RNAP_INS2-RIF相互作用的平均值相比,对接到RNAP_wt-RIF结合位点指示了对RNAP_wt-RIF相互作用的更大的亲和力。
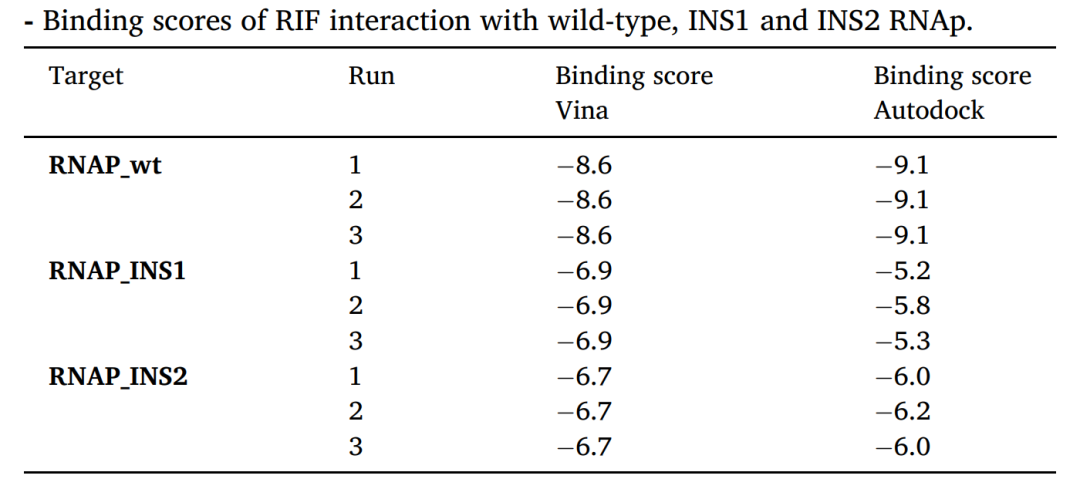
RNAP_wt(浅蓝)、RNAP_INS1(红色)和RNAP_INS2(藏青蓝)结构的拟合示意图
9株携带12nt插入的临床分离株的MIC值为≥32
mg/L,分别测定了2株12nt插入的临床分离株 (GI=38.5h)、3株野生型临床分离株 (GI=20h)和1株敏感对照株(H37Rv) (GI=15h)的平均生长指数。插入株的生长速度比野生型和H37Rv株分别慢1.95和2.5倍,表现出适应性劣势。
结 果

聊生信复现
从头分析获得的VCF文件中记录的变异 (服从NGS左移原则,变异位置:761110)
灰色:利福平;浅蓝:野生;红色:INS1;紫色:INS2

— 基本概念 —
— 文献解读 —
— 数据库 —
ClinVar数据库详解
在线人类孟德尔遗传 (OMIM)数据库简介
— 期刊 —
— 分析技术 —
Jalview多序列比对图中显示序列标识
Linux操作系统结构及常用命令
设置RStudio-Server不频繁掉线
RStudio-Server安装和内网穿透要点
Linux服务器的磁盘概念与相关操作 (一)
Linux服务器的磁盘概念与相关操作 (二)
临床基因组家系数据分析实战,快速发表SCI文章
雇人代写论文是否犯法?
中华人民共和国人类遗传资源管理条例
— Tales of Genetics —

第 3 期临床基因组家系分析,助力发表Case Report